
Laber先天性黑矇(Leber congenital amaurosis, LCA)是一种严重的致盲性遗传性视网膜疾病,多数呈常染色体隐性遗传,患儿通常在出生时或出生后2一3个月就出现严重的视力障碍。
2019年Morgan L. Maeder等发表“Development of a gene-editing approach to restore vision loss in Leber congenital amaurosis type 10 ”的研究论文,该论文已被在国际知名医学期刊Nature medicine(Q1,IF=26.77)接收并在线发表。
研究背景:2017年12月10日,FDA批准了Spark公司AAV基因疗法,通过AAV病毒载体,将正确的RPE65基因递送到视网膜细胞,从而治疗Leber先天性黑蒙2型,该疗法售价高达85万美元/年。但目前还没有针对Leber先天性黑蒙10型的治疗方法被批准,因为CEP290基因的编码序列长达7.5kb,远超AAV病毒的包装能力(4.7kb),无法通过AAV递送正确编码的CEP290基因的方式来治疗。为克服这一局限,Editas Medicine开发了一种特异于CEP290 IVS26突变的基因编辑策略,使用AAV5载体通过视网膜下注射将saCas9和CEP290特异性gRNA递送至感光细胞,通过双gRNA分别靶向突变内含子区域的上下游,直接将突变内含子区域整体删除或倒位,从而恢复CEP290基因的正常表达。
CEP290蛋白位于光感受器的连接纤毛,在外界盘再生和光信号传传导中起重要作用。LCA10型患者中CEP290最常见的突变是剪切突变IVS26(c.2991+ 1655A>G),这一突变对视网膜光感受细胞的影响较大,而对其他体细胞影响轻微,因此临床表型仅局限于眼部。CEP290包含7.5k个碱基,远远超过AAV载体的介导能力,为了克服基因替代疗法的局限性,研究者通过视网膜下注射的方法,将AAV5载体介导的金黄葡萄球菌Cas9和CEP290特异向导RNA(gRNAs)导入光感受器细胞内,这种gRNAs可以更正原有的IVS26突变,从而正常剪切,得到CEP290的正常表达,并从以下三个方面证明了该方法(EDIT-101)纠正CEP290 IVS26突变的有效性。
一、人体成纤维细胞和视网膜组织体外实验阐明了EDIT-101作用机制人体成纤维细胞和视网膜组织体外实验阐明了EDIT-101作用机制,并且 证明了核酸酶的特异性。SaCas9和gRNA(EDIT-101)转染LCA10患者的成纤维细胞后,野生型CEP290mRNA升高,同时突变型CEP290mRNA降低 ,而且全长的CEP290蛋白表达增加。EDIT-101转染视网膜组织后,也得到了预期的编辑效果,平均编辑率约为41.7±15.9% 。而且这种方法特异性很高,都没有观察到脱靶效应。Fig1 a.EDIT-101的示意图;Fig1b.基因编辑策略示意图;c, 定量PCR qRT–PCR检测体外成纤维细胞野生型(蓝色)和IVS26突变型(橙色)CEP290 mRNA转录本;d.人视网膜组织切片的免疫荧光图片,说明AAV5-hGRK1-GFP体外转染后,在视网膜组织中可以检测到GFP的表达。(图1)

建立CEP290 IVS26基因突变敲入小鼠模型,在小鼠模型视网膜下注射EDIT-101,观察剂量效应和药代动力学,检测到迅速并且持久的基因编辑效果,而且总体CEP290基因编辑率与 SaCas9 mRNA和gRNA均相关(图2)。
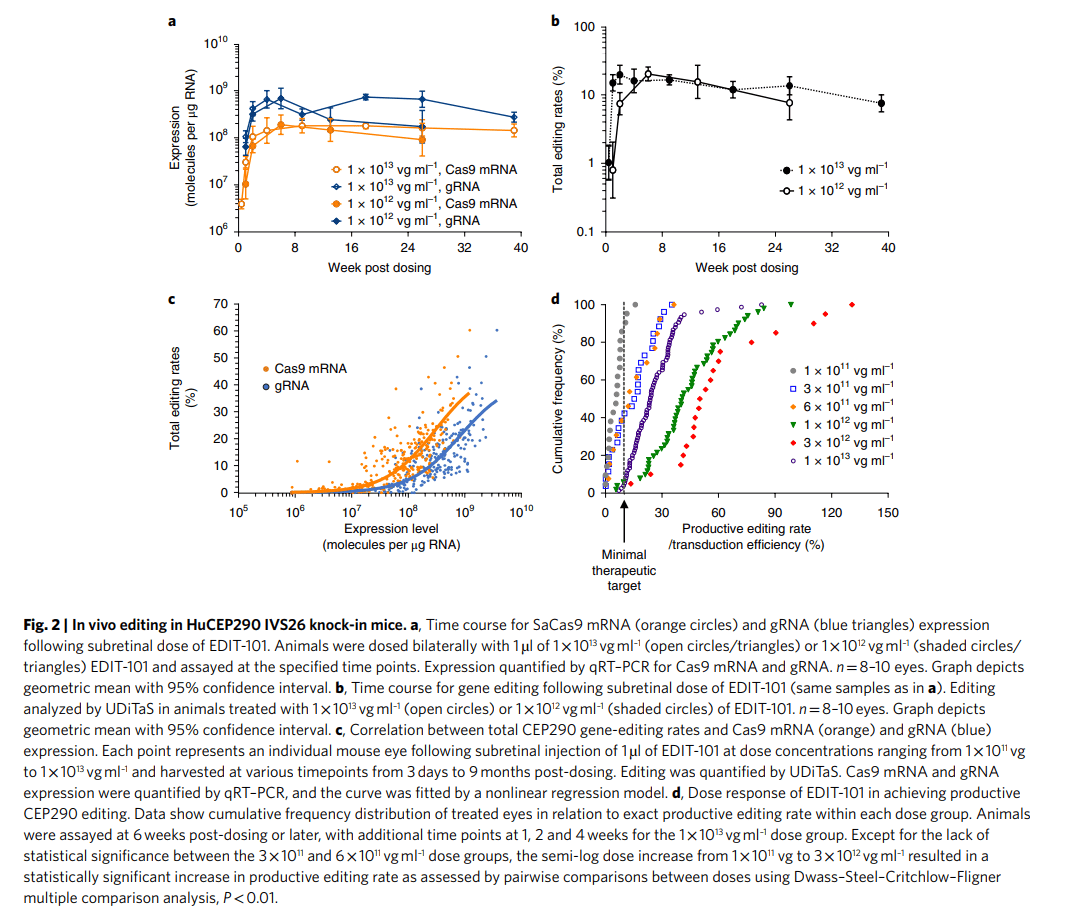
图2.HuCEP290 IVS26敲入小鼠的体内编辑效果。a.不同浓度EDIT-101在小鼠视网膜下注射后不同时间点Cas9 mRNA和gRNA的表达;b.不同药物浓度注射后不同时间点基因编辑的比例;c.CEP290总体基因编辑率和Cas9 mRNA (橙色)、gRNA (蓝色)的相关性。d.达到有效CEP290编辑的EDIT-101的剂量反应。
三、小鼠缺少黄斑结构,而EDIT-101的设计主要是为了恢复部分视锥细胞功能小鼠缺少黄斑结构,而EDIT-101的设计主要是为了恢复部分视锥细胞功能,因此研究者又设计了用于灵长类动物的EDIT-101类似物(VIR026 and VIR067),并在灵长类动物中证明了其对CEP290基因编辑的有效性,达到了治疗效果的阈值,表明 CRISPR/Cas9技术可以在灵长类动物体细胞中进行有效编辑(图3)。a-d.灵长类动物黄斑旁视网膜下注射VIR607(治疗组)或者平衡盐溶液(对照组)后,SaCas9仅在治疗眼的光感受器细胞中表达。
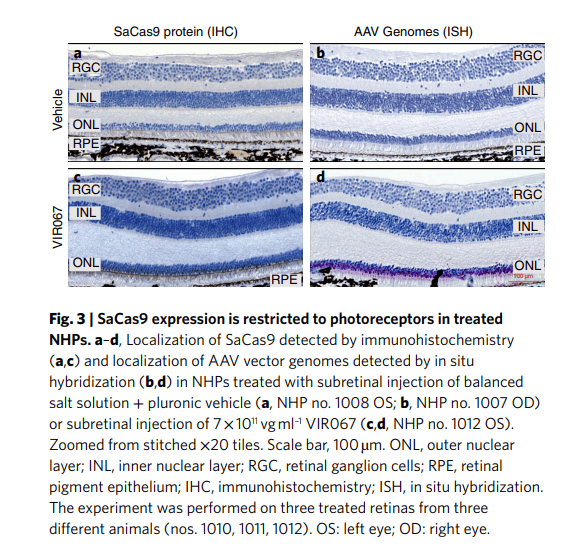
图3.在处理过非人灵长类模型中,SaCas9的表达仅限于光感受器

表1不同剂量EDIT-101类似物对小鼠和NHPs的编辑效率
作者还比较了不同浓度剂量的药物在小鼠和灵长类动物中的基因编辑率,临床认为基因编辑率>10%即能提高患者的视功能,因此从下表可见当药物浓度达到1*1012vg/ml时,便可显著超过临床治疗有效的阈值。
研究小结:研究者阐明基因编辑新药EDIT-101的原理、药理作用以及耐受性等,为EDIT-101研发和下一步临床实验奠定了基础。而且这项研究表明EDIT-101在灵长类动物中无明显免疫反应,并且没有观察到脱靶效应,安全性好。这项研究不仅可能造福CEP290相关LCA的患者,而且为其他基因相关的视网膜变性疾病也提供了新思路。
相关信息:Leber先天性黑矇(LCA)作为一种重要的视网膜变性类疾病,其发病早、危害重,给社会带来了沉重负担。因此也有越来越多的学者关注于相关疾病的研究,其中典型的代表是RPE65相关LCA的基因替代治疗,相关药物LUXTURNA目前在美国已上市而且表现出良好的治疗效果。但是视网膜变性类疾病发病机制复杂,很多疾病并不适合套用基因替代治疗,比如本文中提到的CEP290,因其碱基数目庞大,常规的病毒载体难以介导正常CEP290基因转染。但是CEP290基因有突变热点,因此本文作者有针对性的设计了相应的基因编辑药物,可以用于治疗因此热点突变导致的视网膜疾病。我们在受此鼓舞的同时必须清晰的认识到,CEP290突变在中国人群中突变率不高,本文提到的热点突变目前尚未在我国人群中发现,因此此药很可能不适用于中国的患者。因此针对遗传性视网膜疾病,我们需要根据不用的遗传背景和机制,来研究相应的治疗方法,不能完全照搬国外的技术,需要因地制宜,因病施药。
信源:
Morgan L, Maeder,Michael, Stefanidakis,Christopher J, Wilson et al. Development of a gene-editing approach to restore vision loss in Leber congenital amaurosis type 10.[J] .Nat Med, 2019, 25: 0.
参考文献
1. Chang, B. et al. In-frame deletion in a novel centrosomal/ciliary protein CEP290/NPHP6 perturbs its interaction with RPGR and results in early-onset retinal degeneration in the rd16 mouse. Hum. Mol. Genet. 15, 1847–1857 (2006).
2. Drivas, T. G. & Bennett, J. CEP290 and the primary cilium. Adv. Exp. Med. Biol. 801, 519–525 (2014).
3. Stone, E. M. Leber congenital amaurosis - a model for efcient genetic testing of heterogeneous disorders: LXIV Edward Jackson Memorial Lecture. Am. J. Ophthalmol. 144, 791–811 (2007).
4. Stone, E. M. et al. Clinically focused molecular investigation of 1000 consecutive families with inherited retinal disease. Ophthalmology 124, 1314–1331 (2017).
5. Drivas, T. G., Wojno, A. P., Tucker, B. A., Stone, E. M. & Bennett, J. Basal exon skipping and genetic pleiotropy: a predictive model of disease pathogenesis. Sci. Transl. Med. 7, 291ra297 (2015).
6. den Hollander, A. I. et al. Mutations in the CEP290 (NPHP6) gene are a frequent cause of Leber congenital amaurosis. Am. J. Hum. Genet. 79, 556–561 (2006).
7. Collin, R. W. et al. Antisense oligonucleotide (AON)-based therapy for Leber congenital amaurosis caused by a frequent mutation in CEP290. Mol. Ter. Nucleic Acids 1, e14 (2012).
8. Gerard, X. et al. AON-mediated exon skipping restores ciliation in fbroblasts harboring the common Leber congenital amaurosis CEP290 mutation. Mol. Ter. Nucleic Acids 1, e29 (2012).
9. Parftt, D. A. et al. Identifcation and correction of mechanisms underlying inherited blindness in human iPSC-derived optic cups. Cell Stem Cell 18, 769–781 (2016).
10. Coppieters, F., Lefever, S., Leroy, B. P. & De Baere, E. CEP290, a gene with many faces: mutation overview and presentation of CEP290base. Hum. Mutat. 31, 1097–1108 (2010).
11. Boye, S. E. et al. Natural history of cone disease in the murine model of Leber congenital amaurosis due to CEP290 mutation: determining the timing and expectation of therapy. PLoS ONE 9, e92928 (2014).
12. Geller, A. M. & Sieving, P. A. Assessment of foveal cone photoreceptors in Stargardt’s macular dystrophy using a small dot detection task. Vision Res. 33, 1509–1524 (1993).
13. Geller, A. M., Sieving, P. A. & Green, D. G. Efect on grating identifcation of sampling with degenerate arrays. J. Opt. Soc. Am. A. 9, 472–477 (1992).
14. Garanto, A. et al. Unexpected CEP290 mRNA splicing in a humanized knock-in mouse model for Leber congenital amaurosis.
PLoS ONE 8, e79369 (2013).
15. Cideciyan, A. V. et al. Centrosomal-ciliary gene CEP290/NPHP6 mutations result in blindness with unexpected sparing of photoreceptors and visual brain: implications for therapy of Leber congenital amaurosis. Hum. Mutat. 28, 1074–1083 (2007).
16. Cideciyan, A. V. et al. Cone photoreceptors are the main targets for gene therapy of NPHP5 (IQCB1) or NPHP6 (CEP290) blindness: generation of an all-cone Nphp6 hypomorph mouse that mimics the human retinal ciliopathy. Hum. Mol. Genet. 20, 1411–1423 (2011).
17. Boye, S. E. et al. Te human rhodopsin kinase promoter in an AAV5 vector confers rod- and cone-specifc expression in the primate retina. Hum. Gene Ter. 23, 1101–1115 (2012).
18. LUXTURNA (voretigene neparvovec-rzyl, package insert) (Spark Terapeutics, 2017).
19. Giannoukos, G. et al. UDiTaS, a genome editing detection method for indels and genome rearrangements. BMC Genomics 19, 212 (2018).
20. Burnight, E. R. et al. CEP290 gene transfer rescues Leber congenital amaurosis cellular phenotype. Gene Ter. 21, 662–672 (2014).
21. Feodorova, Y., Koch, M., Bultman, S., Michalakis, S. & Solovei, I. Quick and reliable method for retina dissociation and separation of rod photoreceptor perikarya from adult mice. MethodsX 2, 39–46 (2015).
22. Niesen, F. H., Berglund, H. & Vedadi, M. Te use of diferential scanning fuorimetry to detect ligand interactions that promote protein stability. Nat. Protoc. 2, 2212–2221 (2007).
23. Kim, D. et al. Digenome-seq: genome-wide profling of CRISPR-Cas9 of-target efects in human cells. Nat. Methods 12, 237–243 (2015).
24. Park, J. et al. Digenome-seq web tool for profling CRISPR specifcity. Nat. Methods 14, 548–549 (2017).
25. Tsai, S. Q. et al. GUIDE-seq enables genome-wide profling of of-target cleavage by CRISPR-Cas nucleases. Nat. Biotechnol. 33, 187–197 (2015).
26. Friedland, A. E. et al. Characterization of Staphylococcus aureus Cas9: a smaller Cas9 for all-in-one adeno-associated virus delivery and paired nickase applications. Genome Biol. 16, 257 (2015).
27. Martin, M. Cutadapt removes adapter sequences from high-throughput sequencing reads. EMBO J. 17, 10–12 (2011).
28. Langmead, B. & Salzberg, S. L. Fast gapped-read alignment with Bowtie 2. Nat. Methods 9, 357–359 (2012).
29. Li, H. et al. Te sequence alignment/Map format and SAMtools. Bioinformatics 25, 2078–2079 (2009).
30. Bothmer, A. et al. Characterization of the interplay between DNA repair and CRISPR/Cas9-induced DNA lesions at an endogenous locus. Nat. Commun. 8, 13905 (2017).
31. Kleinstiver, B. P. Engineered CRISPR-Cas9 nucleases with altered PAM specifcities. Nature 523, 481–485 (2015).
32. Bae, S., Park, J. & Kim, J. S. Cas-OFFinder: a fast and versatile algorithm that searches for potential of-target sites of Cas9 RNA-guided endonucleases. Bioinformatics 30, 1473–1475 (2014).
END
文案 | 刘卫勤
排版 | 姜笑南
审核 | 姜笑南
发布|姜笑南
世界生命科学大会
RECRUIT
关注我们,获取生命科学
学界前沿|促进更多的学术交流与合作
业界前沿|促进更快的产品创新与应用
政策前沿|促进更好的治理实践与发展
我们期待你的加入
